如圖為genomic DNA 經過bisulfite conversion 後,利用圖中所示探針進行 MethyLight 分析所得之擴增曲線,下列敘述何者最不適當?
詳細解析
本題觀念:
本題聚焦於 MethyLight(甲基化特異性實時定量 PCR)技術之原理:利用 sodium bisulfite 處理後的 DNA,將未甲基化的胞嘧啶(C)轉化為尿嘧啶(U,再於 PCR 中呈現為 T),而保留 5-methylcytosine 於 CpG 位點,使得設計含有 CpG 的探針或引子只會與甲基化序列完全互補並產生訊號,透過探針螢光強度與循環數關係判讀該位點之甲基化程度。
影像分析:
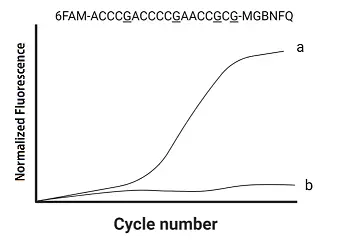
圖中呈現兩條擴增曲線,曲線 a 在第十多個循環即進入指數增幅期,螢光強度顯著上升;曲線 b 始終接近背景而無擴增。由上方標示的探針序列 “6FAM-ACCCGACCCCGAACCGCG-MGBNFQ” 可見其含有多個 CpG 位點,僅在這些胞嘧啶被甲基化、 bisulfite 處理後仍保有 “CG” 配對時,探針才能完全互補偵測,PCR 才順利進行並產生螢光。因此曲線 a 代表樣本中該區域為甲基化狀態;曲線 b 則代表該區幾乎無甲基化訊號。
選項分析
-
選項A “此區域中有 4 個 CpG 位點”:從探針序列 ACCCGACCCCGAACCGCG 中,以 C (第4位)–G(第5位)、C(第10位)–G(第11位)、C(第15位)–G(第16位)、C(第17位)–G(第18位) 等共 4 組 CpG 二核苷酸,可確定此區含 4 個 CpG,屬實。
-
選項B “可用於檢測腫瘤檢體中抑癌基因啟動子區域是否有高度甲基化的現象”:MethyLight 廣泛應用於 MGMT、MLH1、CDKN2A(p16) 等抑癌基因啟動子甲基化檢測,靈敏度高且能量化低頻率的甲基化事件,臨床常用於癌症早期診斷與預後評估(pubmed.ncbi.nlm.nih.gov)。
-
選項C “a 曲線是基因啟動子區域沒有甲基化的結果”:事實上,只有當 CpG 位點被甲基化,bisulfite 處理後保留 “C”,探針才能與模板完全互補並偵測到螢光增幅;曲線 a 正是甲基化所致,故此敘述最不適當。
-
選項D “可選用富含 CpG 位點的 Alu elements 來作為 DNA input control”:MethyLight 協定中常使用 Alu 重複序列作為 QC-1(甲基化獨立)之 DNA input control,因 Alu 在基因組中豐富且能代表整體 DNA 量;雖最終設計的引子/探針迴避 CpG 以不受甲基化影響,但原始 Alu 重複序列確實富含 CpG,適合作為輸入量校正(pmc.ncbi.nlm.nih.gov)。
答案解析
MethyLight 探針設計必須包含 CpG 以區分甲基化(保留 C)和未甲基化(轉為 T)序列;圖中 a 曲線之早期擴增明確顯示探針目標區域存在甲基化訊號,與「沒有甲基化」敘述相反,故選項 C 最不適當。其餘選項皆符合 MethyLight 技術特性與臨床應用,包括 CpG 數目判讀、腫瘤抑癌基因甲基化檢測,以及 Alu 重複序列作為 DNA input control。
核心知識點
- Bisulfite conversion 化學反應:未甲基化 C→U(T),5-methylcytosine 保留 C
- MethyLight 原理:甲基化特異性引子/探針結合 → real-time PCR 螢光偵測
- CpG site 計算與序列設計:探針需含 CpG,數目即為可檢測的位點
- Ct 值/擴增曲線判讀:早期擴增 (低 Ct) 代表甲基化;無擴增 (高 Ct 或無訊號) 代表低或無甲基化
- QC 控制反應:QC-1 使用 Alu elements(CpG-rich 重複序列,設計後迴避 CpG 以利輸入量校正)
- 臨床應用:抑癌基因(MGMT、MLH1、p16/CDKN2A 等)啟動子高甲基化檢測與預後評估
以上知識為掌握數位甲基化分析與 MethyLight 技術的基礎,準備相關考題或臨床檢測時須熟悉。