以次世代定序進行遺傳基因檢測,利用已知變異的參考物質,計算可偵測範圍中的每種變異的準確度,整理檢測結果如圖所示。下列計算何者正確?
詳細解析
本題觀念:
此題核心在於從混淆矩陣(confusion matrix)推導各種診斷測試性能指標,包括敏感度(sensitivity)、特異度(specificity)、陽性預測值(PPV)、陰性預測值(NPV)、偽陽性率(FPR)、偽陰性率(FNR)以及正向/負向一致率(PPA/NPA)。題幹額外加入「無偵測(no calls)」欄位,考生須理解何者納入分母、何者排除,才能正確套用公式。
影像分析:
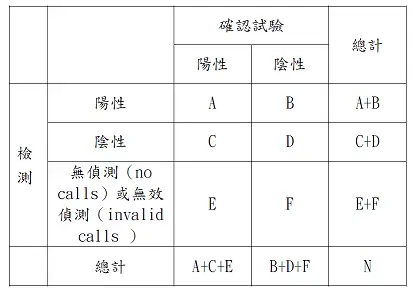
表格各象限含義如下
- 真陽性(TP)=A:檢測陽性且參考試驗陽性
- 假陽性(FP)=B:檢測陽性但參考試驗陰性
- 假陰性(FN)=C:檢測陰性但參考試驗陽性
- 真陰性(TN)=D:檢測陰性且參考試驗陰性
- 無效偵測對陽性參考=E,對陰性參考=F
- 各行列合計亦標示於表格,總樣本數 N=A+B+C+D+E+F
此混淆矩陣特別加入「無偵測/無效偵測」類別,提示有些指標計算時需排除此類結果。
選項分析
-
選項A 陽性一致率: A/(A+C+E)
PPA(Positive Percent Agreement)標準公式為A/(A+C),排除無效呼叫(E) (ncss.com)。此選項誤將E納入,計算錯誤。 -
選項B 陽性預測值: A/(A+C)
PPV(Positive Predictive Value)=A/(A+B) (nejm.org)。此選項將C(FN)誤置於分母,錯誤。 -
選項C 偽陰性率: 1−[A/(A+C)]
FNR(False Negative Rate)=FN/(TP+FN)=C/(A+C)=1−sensitivity=1−A/(A+C) (ncss.com)。公式正確。 -
選項D 偽陽性率: 1−[D/(B+D+F)]
FPR(False Positive Rate)=FP/(FP+TN)=B/(B+D)=1−specificity=1−D/(B+D) (nejm.org)。此選項誤將F納入且計算的是負向預測值(NPV)的補數,並非FPR,故錯誤。
答案解析
偽陰性率定義為所有實際有病(參考陽性)中,檢測錯誤判為陰性的比例:C/(A+C)。等價於1−sensitivity(1−A/(A+C))。選項C唯一符合此標準公式,其餘選項非以正確分母計算或將無效呼叫納入、導致計算結果不符定義。
核心知識點
- 混淆矩陣六要素:A(TP)、B(FP)、C(FN)、D(TN)、E/F(無效呼叫)
- Sensitivity(True Positive Rate)=A/(A+C)
- Specificity(True Negative Rate)=D/(B+D)
- PPV=Positive Predictive Value=A/(A+B)
- NPV=Negative Predictive Value=D/(C+D)
- False Positive Rate=FP/(FP+TN)=B/(B+D)=1−specificity
- False Negative Rate=FN/(TP+FN)=C/(A+C)=1−sensitivity
- PPA/NPA計算時通常排除無效呼叫
臨床重要性
正確掌握這些測試性能指標,是評估次世代定序等高階檢測方法可靠度的基礎。公式套用若有誤,將直接影響對檢測靈敏度與特異度的判斷,進而可能誤導基因變異偵測結果的臨床解讀與後續病人管理。