112年:(醫檢)檢驗(1)
如圖所示為利用 DNA 甲基化晶片進行實驗分析的結果,下列敘述何者最正確?
A重亞硫酸鹽主要是將具有甲基化的胞嘧啶(cytosine)轉變為尿嘧啶(uracil)
B通常在基因的啟動子(promoter)處如果有高度甲基化,會伴隨該基因高度表現
C以甲基化晶片可以同時定量多個CpG位點(CpG site)
D甲基化是表觀遺傳調控(epigenetic regulation)的一種,透過改變基因序列造成突變的方式達到基因表達調控
詳細解析
本題觀念
本題考查 DNA 甲基化 (DNA methylation) 的生化原理與微陣列 (methylation microarray) 技術,重點在於重亞硫酸鹽 (bisulfite) 處理能區分甲基化與未甲基化的胞嘧啶,以及利用甲基化晶片同時定量大量 CpG 位點的高通量特性。
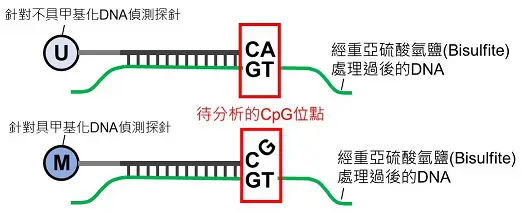
影像分析
圖片示意 Bisulfite 處理前後的 DNA 序列差異:
- 未甲基化 DNA(上方,U):原序列中 C(胞嘧啶)經 Bisulfite 去氨基化後變成 U(尿嘧啶),PCR 扩增後作為 T(胸腺嘧啶),因此探針結合序列從 CAGT → TAGT。
- 甲基化 DNA(下方,M):5-methylcytosine 受甲基保護,不被 Bisulfite 轉換,保留 GC 序列 (CGGT),因此探針結合序列不變。
紅框處標示「待分析的 CpG 位點」,微陣列上亦相對應設有「M 探針」與「U 探針」。根據雜交後的螢光強度比值就可推算該 CpG 的甲基化百分比。
選項分析
- 選項A
誤將 Bisulfite 轉換目標對象顛倒。實際上,Sodium Bisulfite 只將未甲基化的 cytosine 去氨基成 uracil,而5-methylcytosine 因甲基保護而不受影響,不會被轉換 ([illumina.com](http
...(解析預覽)...